Související příspěvek
ChIP-Seq Řešení problémů 101: Krok za krokem opravte slabý signál
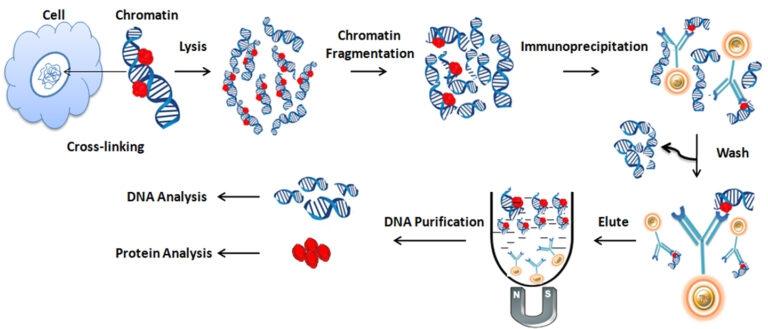
2026-02-28Řešení problémů ChIP-Seq často začíná jedním jednoduchým příznakem – nízkým signálem – ale skutečné příčiny jsou obvykle rozloženy mezi kvalitu chromatinu, výkon protilátek, podmínky imunoprecipitace a kvalitu knihovny. Ve společnosti Longlight Technology podporujeme laboratoře, které používají ChIP-Seq pro histonové značky a transkripční faktory, a vidíme opakování stejných "tichých bodů selhání" napříč různými přístroji a typy vzorků. Tento průvodce ChIP-Seq Troubleshooting 101 provádí začátečníky krok za krokem cestou k obnově signálu v logickém pořadí, přičemž využívá praktické kontrolní body, které můžete ověřit v jednom běhu.
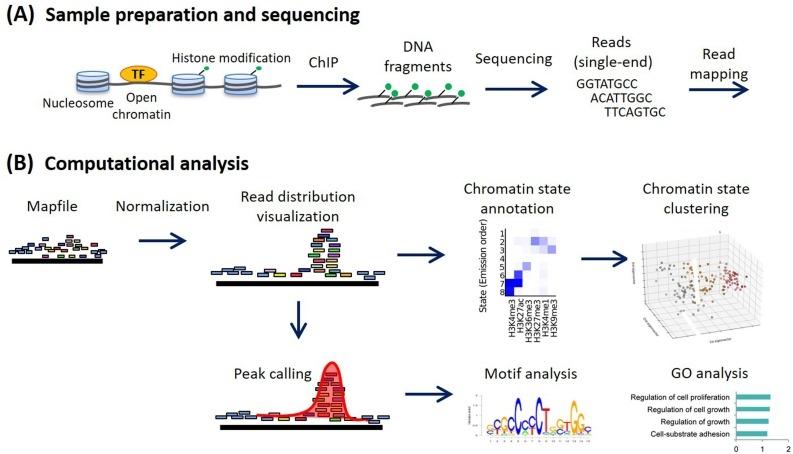
Metody pro analýzu ChIP-seq: Praktický pracovní postup a pokročilé aplikace - ScienceDirect
1) Definujte "Nízký signál" Než cokoli změníš
Nízký signál může znamenat různé věci: příliš málo vrcholů, slabé obohacení na známých lokusech, nebo knihovnu, která vypadá dobře, ale špatně se mapuje. Dobré řešení problémů s ChIP-Seq začíná jasným označením režimu selhání, protože každý režim ukazuje na jiné opravy.
Vhodný způsob, jak problém definovat, je zkontrolovat tři vrstvy:
✓ Biologická vrstva: Je cíl přítomen ve vašem buněčném stavu (stimulovaný vs. v klidu, diferenciační fáze, načasování léčby)?
✓ Vrstva obohacení: Vykazuje ChIP DNA obohacení qPCR na pozitivně kontrolovaném místě oproti negativní oblasti?
✓ Sekvenační vrstva: Máte dostatek unikátních, mapovaných čtení a rozumnou úroveň duplikátů?
Pokud na tyto tři odpovědi neodpověděli, neoptimalizujte všechno. Nejprve proveďte jeden kontrolovaný experiment: nechte vzorek stejný, hloubku sekvenace nechte skromnou a změňte pouze jednu podezřelou proměnnou.
2) Začněte s chromatinem: velikost fragmentu and Loss Control
Když se laboratoře ptají, proč ChIP "nefunguje", nejčastější příčinou je chromatin, který je nadměrně fragmentovaný, podfragmentovaný nebo jednoduše ztracený během čištění. V ChIP-Seq řešení problémů je chromatin základem – pokud je nekonzistentní, každý další krok se změní v šum.
Pro workflow založené na sonikaci mnoho laboratoří cílí na fragmenty v rozmezí ~150–300 bp pro ostré volání vrcholů a konzistentní imunoprecipitaci. Pokud jsou fragmenty většinou větší (například >500 bp), protilátky mají problém efektivně strhnout cílové komplexy. Pokud jsou fragmenty příliš malé, můžete zničit epitopy nebo zvýšit pozadí uvolněním nespecifické DNA.
Praktické kontrolní body, které můžete udělat hned:
• Měření DNA po reverzním křížovém propojení a čištění (nejen před IP). Velký pokles zde signalizuje ztrátu korálků/sloupců nebo drsné podmínky.
• Porovnávat fragmentační profily napříč vzorky. Pokud je jeden vzorek "dokonalý" a další je rozmazaný nebo předimenzovaný, zaměřte se na nastavení lýzy a sonikace, ne na protilátku jako první.
• Uchovat aliquot "vstupní DNA" z každé dávky. To je vaše výchozí hodnota pro qPCR i knihovní kontrolu.
V Longlight Technology doporučujeme přistupovat k přípravě chromatinu jako k kontrolovanému výrobnímu kroku: opravit složení pufru, udržovat stabilní teplotu vzorku během sonifikace a zaznamenat přesné nastavení cyklu. Malé odchylky později způsobují velké rozdíly v maximální síle.
3) Shoda protilátek: Specifita, variace v dávce, and Ovládací prvky
Pokud chromatin vypadá rozumně, dalším krokem v ChIP-Seq řešení problémů je výběr a validace protilátek. Nízký signál je často způsoben použitím protilátky, která je "dobrá pro západ", ale slabá pro ChIP, nebo variabilitou mezi jednotlivými záložemi.
Dobrá strategie s protilátkami je postavena na kontrolách:
✓ Pozitivní kontrolní cíl: histonová značka s robustním obohacením (běžně používaná k potvrzení zdraví pracovního postupu).
✓ Negativní regulace: IgG nebo izotypová kontrola pro odhad pozadí pulldown.
✓ Známé lokusy qPCR: jeden nebo dva publikované pozitivní lokusy pro váš cíl, plus oblast genové poušti.
U transkripčních faktorů může být signál inherentně nižší než histonové značky. To znamená, že vaše protilátka musí mít vysokou afinitu a vaše duševní zdraví musí být čisté. Pokud jste v TF ChIP noví, nezačínejte měnou hloubky sekvenace. Nejprve potvrďte obohacení pomocí qPCR. Pokud je qPCR obohacení slabé, více čtení většinou přinese více šumu.
Praktický tip: Když měníte dávky protilátek, pokud možno znovu zkontrolujte obohacení na stejné dávce chromatinu. Pokud změna šarže naruší signál, workflow nemusí být nutně "špatný" – změnil se výkon vašeho činidla a vaše cesta k řešení problémů by to měla odrážet.
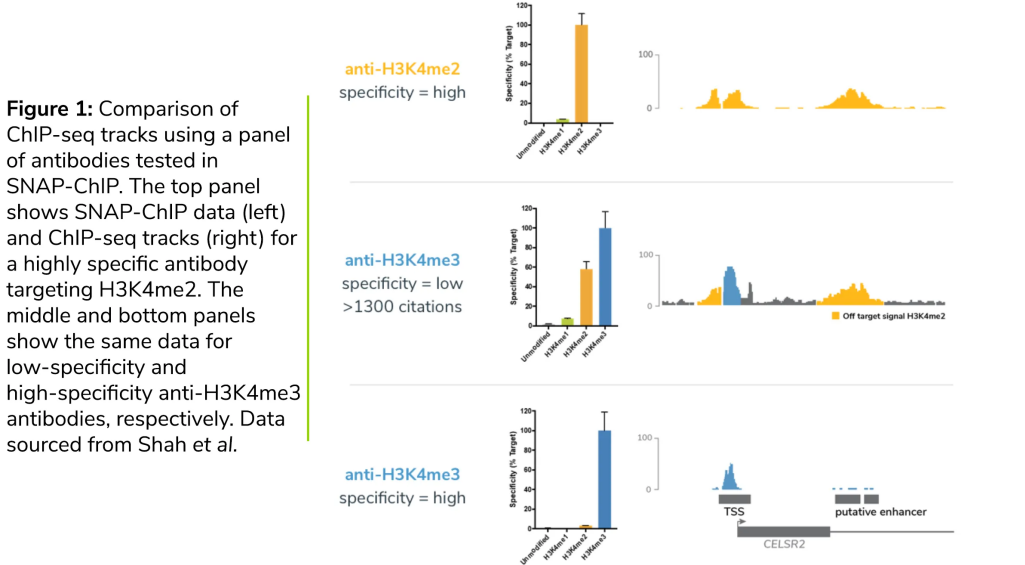
Výběr správné ChIP protilátky pro váš experiment - EpiCypher
4) Čistá sekvence optimalizace IP – žádné odhady
Kromě chromatinu a protilátek je dalším klíčovým bodem chemie IP (korálky, washe, inkubace). Slabý signál je často problém v pozadí.
✓ Výběr korálků: Vyberte protein A/G, který odpovídá vašemu druhu/izotypu protilátky.
✓ Množství protilátek: Titrovat, aby se předešlo slabému pull-down nebo zvýšené nespecifické DNA.
✓ Vyvážení wash: Kalibrujte přísnost pro odstranění šumu a zároveň zachování slabých, ale skutečných interakcí.
Praktické pravidlo pro začátečníky je upravovat pouze jednu osu na běh:
• Pokud vrcholy existují, ale jsou slabé, zvyšuje se efektivní zachycení (o něco více protilátek, lepší vázání kuliček, delší inkubace).
• Pokud jsou píky široké a hlučné, zvyšte specificitu (silnější washe, lepší blokace, snížení přetížení protilátkami).
Z pohledu výrobce navrhuje Longlight Technology imunodacypační činidla a systémy magnetických kuliček tak, aby minimalizovala ztráty při manipulaci, protože ztráta vzorku vypadá přesně jako "nízký signál". Hladké oddělení kuliček, konzistentní vázání a čisté kroky mytí snižují variabilitu mezi operátory – což je obzvlášť důležité pro týmy školící nové zaměstnance.
5) Knihovní kontrola kvality: Kdy "Dobrá DNA" Stále dává slabý signál
Někdy je obohacení ChIP DNA skutečné, ale výsledná data stále vypadají plochě. V řešení problémů ChIP-Seq to obvykle odkazuje na metriky konstrukce nebo sekvenování knihoven.
Běžné příčiny nízkého signálu na úrovni knihovny:
✓ Nadměrná amplifikace: příliš mnoho PCR cyklů může zvětšit duplicity a snížit použitelné unikátní čtení.
✓ Artefakty adaptéru/primeru: tyto spotřebovávají sekvenční čtení bez zlepšení pokrytí cíle.
✓ Špatná složitost: často způsobena velmi nízkým vstupem nebo ztrátou ChIP DNA během čištění.
Co zkontrolovat, než znovu spustíte celý ChIP:
• Rozdělení velikosti knihovny (chcete čistý vrchol, ne více neočekávaných vrcholů).
• Rychlost duplicitního a jedinečného mapování po zarovnání.
• Podíl měření v špičkách (FRiP) vůči tvé vnitřní základní hodnotě (i začátečníci mohou sledovat "lepší vs horší" napříč běhy).
Pokud máte podezření na nadměrné cyklování v knihovně, jednoduchým zlepšením je snížit počet cyklů a zvýšit efektivitu záznamu v předchozím procesu (lepší obnova chromatinu a specifika IP). Hloubější sekvenování nemůže kompenzovat knihovnu s nízkou složitostí.
6) Krok-Autor-Obnova signálu Step Signal Můžete začít zítra
Praktická sekvence, která překoná ad-hoc úpravy:
✓ Krok 1: Ověřit, že fragmenty chromatinu mají hodnotu ~150–300 bp a potvrdit obnovu DNA po reverzním křížovém propojení.
✓ Krok 2: Zkontrolujte obohacení qPCR na jednom pozitivním a jednom negativním místě před přípravou knihovny.
✓ Krok 3: Přidejte správné ovládací prvky (vstupní IgG), abyste oddělili "žádné obohacení" od "vysokého pozadí".
✓ Krok 4: Ladit podmínky IP po jedné proměnné (korálky, množství protilátek, pružnost praní).
✓ Krok 5: Auditujte metriky knihovny (duplikace, mapování, rozdělení velikosti) před tím, než předpokládáme, že problém je v sekvenci.
CTA (Longlight Technology): Pokud chcete rychlejší cestu, kontaktujte Longlight Technology pro kontrolní seznam řešení problémů s ChIP-Seq a diagnostický list vzorek po vzorku (knihovna → chromatin → IP). Můžeme také doporučit návrh řízení a strategii párování činidel, která snižuje variabilitu operátora a pomáhá začátečníkům dosáhnout stabilního obohacení dříve.
Nízký signál je frustrující, ale málokdy je záhadný. S disciplinovaným postupem ChIP-Seq řešení problémů – začínající integritou chromatinu, poté přizpůsobením protilátek, specificitou IP a nakonec knihovní kontrolou kvality – můžete z jednoho slabého běhu udělat opakovatelný protokol, který škáluje napříč vzorky, zaměstnanci a projekty.